近日,必赢官网生命科学学院孙士生教授领衔的疾病糖蛋白质组学研究团队取得系列重要进展。团队自主研发出面向高精度糖蛋白质组学研究的专用数据挖掘平台StrucGAP,并系统绘制完成小鼠24种组织的高精度N-糖蛋白质组图谱,从分析方法创新与基础数据资源建设两个维度,为糖蛋白质组学研究提供了系统性解决方案与技术支撑。
糖基化作为最普遍、最重要的蛋白质翻译后修饰之一,参与细胞粘附、信号转导及免疫应答等关键生物学过程。近年来,高分辨率质谱技术和糖肽鉴定算法持续进步,推动糖蛋白质组学进入数据快速积累的新阶段。然而,“上游鉴定工具快速迭代,下游系统分析长期缺位”仍是该领域面临的突出问题。
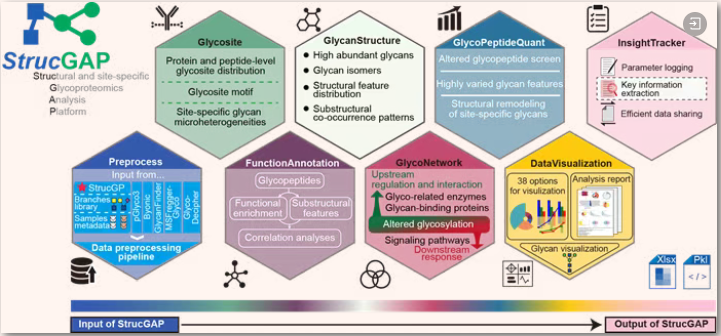
针对这一关键空白,团队在研究中逐步形成了一套系统的高精度糖蛋白质组学数据挖掘策略(Wu Y, Redox Biology, 2025; Zhang Z, Advanced Science, 2025),并借此开发了StrucGAP数据挖掘平台。该平台采用模块化设计,集成数据预处理、糖蛋白/糖基化位点表征、聚糖结构解析、糖肽定量差异分析、功能注释、糖基化调控/互作网络构建、可视化报告输出以及关键信息提取八大核心模块,贯通了糖蛋白质组生物信息学的完整分析流程。作为糖蛋白组学领域首个模块化且可溯源的分析平台,StrucGAP默认输出600余项分析结果,内置39种可视化工具,并自动生成5类共计40页数据分析报告,实现了从原始鉴定结果到生物学机制线索提炼的高效贯通。
目前,StrucGAP已正式开源(https://strucgap.readthedocs.io/en/latest/index.html)。
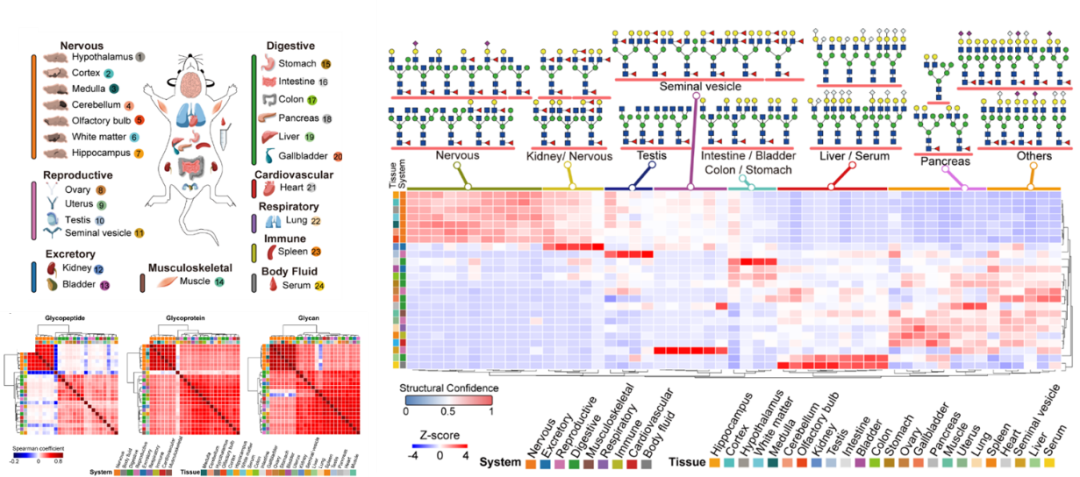
同时,团队采用自主开发的StrucGP软件(Shen J, Nature Methods, 2021),结合大数据挖掘策略与机器学习置信度评估框架,系统绘制了小鼠24种组织(涵盖16个主要器官、7个不同脑区及血清)的N-糖蛋白质组图谱,共鉴定出74,277个完整N-糖肽,覆盖8,681个N-糖基化位点、5,026种糖蛋白及3,045种N-糖链结构,构建了迄今为止覆盖范围最广、结构解析最精细的小鼠组织特异性N-糖基化资源库。
该图谱揭示了N-糖链结构呈现显著组织特异性,可精准区分组织来源,且位点特异性N-糖基化在组织身份识别中的判别能力优于蛋白质组与整体糖组。研究还发现,糖链结构微不均一性的形成并非随机,而是存在明确的“优先搭配”与协同调控规律,为理解糖基化在组织功能特化中的调控机制提供了重要理论基础。
两项成果相互支撑、协同发力,既为糖蛋白质组学数据深度解析提供了标准化、可溯源的分析工具,也构建了目前国际上覆盖最广、精度最高的小鼠组织糖基化基础数据集。StrucGAP 平台将成为连接糖蛋白质组鉴定与生命机制解析的重要桥梁,为疾病糖基化研究、精准医学与人工智能辅助糖组学分析奠定坚实基础;高精度组织图谱则为系统揭示糖基化修饰的组织特异性调控规律提供了全新视角。系列成果的发表,标志着必赢官网在糖蛋白质组学方法学与基础研究领域迈上了新台阶,进一步提升了学校在前沿交叉研究的学术影响力。
两项研究成果接连发表在Nature Communications期刊上,437ccm·必赢国际生命科学学院孙士生教授为两篇论文的通讯作者。

437ccm·必赢国际生命科学学院博士生杨牧垚、吴咏琪、博士毕业生张知达为本论文的共同第一作者。
论文链接:https://www.doi.org/10.1038/s41467-026-70560-7

437ccm·必赢国际生命科学学院博士生吴咏琪、杨牧垚,硕士生徐勇超,和博士毕业生贾丽为本论文的共同第一作者。
论文链接:https://www.nature.com/articles/s41467-025-68186-2
上述成果获得国家自然科学基金重大研究计划培育项目和面上项目(92578129、22374117),以及陕西省自然科学基金特别支持项目和重点项目(2024JC-TBZC-06、2023-JC-ZD-46)的支持。
